© Vladimir LORMAN/Serguei ROCHAL/CNRS Images
Reference
20070001_0976
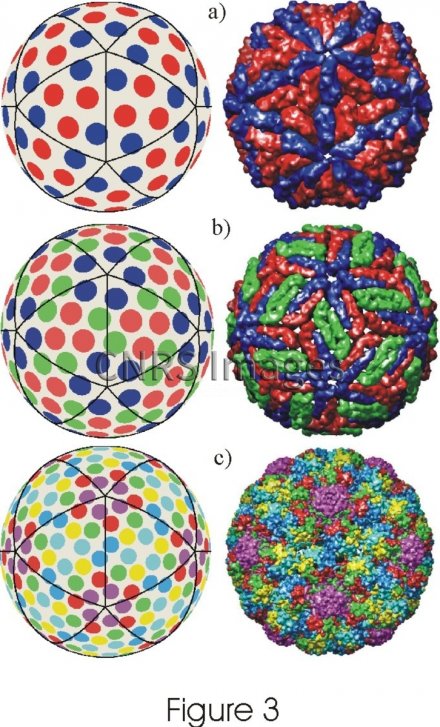
Modélisation de petits virus de forme icosaédrique. Comparaison des positions des centres des protéi
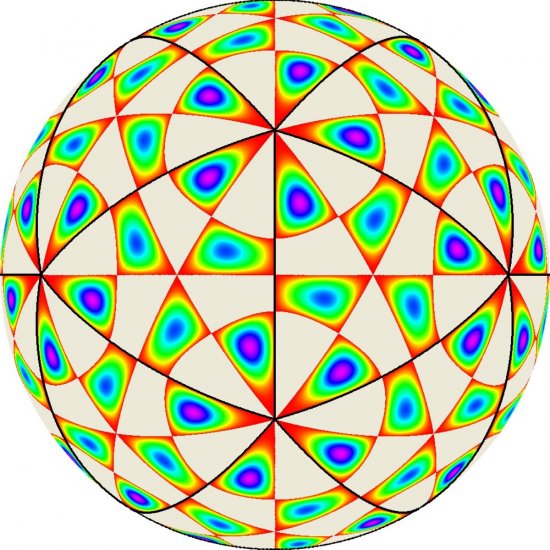
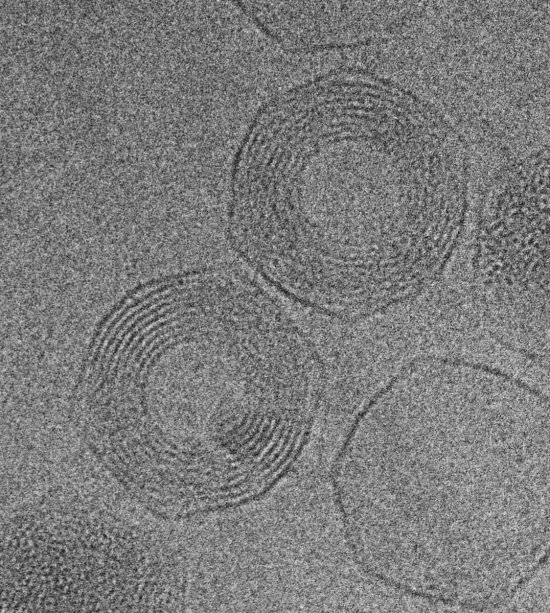
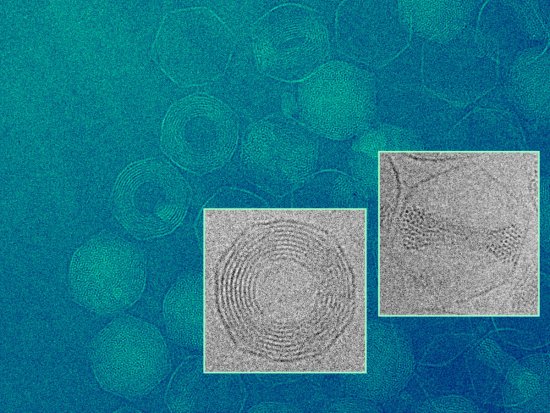
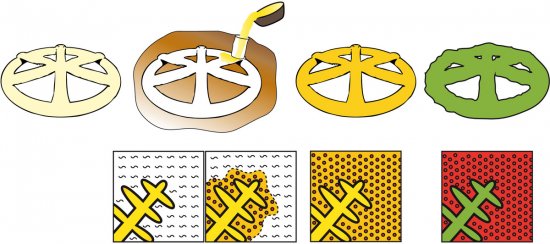
Modélisation de petits virus de forme icosaédrique. Comparaison des positions des centres des protéines prédites par le modèle (à gauche) avec des structures virales expérimentales (à droite) ne satisfaisant pas aux règles géométriques de Caspar et Klug. Des chercheurs ont élaboré une théorie de la formation de ces capsides. On peut ainsi classifier tous les petits virus icosaédriques et rendre compte exactement de la répartition des protéines à leur surface en fonction du nombre de sites de protéines différentes qui la constituent. Calculer cette distribution de surface peut permettre de prédire l'effet de la structure globale sur le pouvoir infectieux du virus. a) Virus L-A ; b) Virus de la dengue ; c) virus du polyome murin.
The use of media visible on the CNRS Images Platform can be granted on request. Any reproduction or representation is forbidden without prior authorization from CNRS Images (except for resources under Creative Commons license).
No modification of an image may be made without the prior consent of CNRS Images.
No use of an image for advertising purposes or distribution to a third party may be made without the prior agreement of CNRS Images.
For more information, please consult our general conditions